Maladies et pathogènes
L'ANRS MIE focalise son action sur la recherche sur le VIH/sida, les hépatites virales, les infections sexuellement transmissibles, la tuberculose et les maladies infectieuses émergentes (en particulier les fièvres hémorragiques virales, les arboviroses et les infections respiratoires émergentes, dont la Covid-19).
Dernière mise à jour le 06 août 2025
Comprendre et combattre les maladies infectieuses
- Les maladies infectieuses résultent de l’invasion et de la prolifération d’agents pathogènes—bactéries, virus, parasites ou champignons—dans un hôte. Leur transmission peut être directe (contact interhumain, gouttelettes respiratoires, fluides biologiques) ou indirecte (vecteurs, eau, aliments contaminés, surfaces inertes).
- Elles constituent un enjeu majeur de santé publique en raison de leur capacité à émerger, se propager rapidement et évoluer sous la pression des interventions thérapeutiques et environnementales.
- L’étude des maladies infectieuses mobilise des approches pluridisciplinaires combinant microbiologie, immunologie, épidémiologie et sciences sociales, afin de comprendre les mécanismes physiopathologiques, d’optimiser les stratégies de surveillance et de développer des outils diagnostiques, thérapeutiques et prophylactiques efficaces.
Découvrez ci-dessous les principales maladies et agents pathogènes pour lesquels l’ANRS MIE s’engage dans des projets de recherche afin d’améliorer leur connaissance, leur prévention, leur diagnostic ou encore leur traitement.
Arboviroses
Les arboviroses sont des maladies dues à des arbovirus (arthropod-borne viruses) transmis par des vecteurs arthropodes.
Chikungunya
Le chikungunya est une maladie infectieuse provoquée par un arbovirus, le virus du chikungunya. Elle peut désormais se rencontrer dans des régions non tropicales, y compris en Europe.
Covid-19
La covid-19 est une maladie infectieuse causée par le coronavirus SARS-CoV-2.

Covid-long
Le Covid-long est une pathologie causée par le SARS-CoV-2 au cours de laquelle les symptômes persistent plus de deux mois.

Dengue
La dengue est une maladie infectieuse due au virus de la dengue, un arbovirus. Il s’agit de l’arbovirose humaine la plus répandue dans le monde.
Fièvres hémorragiques virales
Les fièvres hémorragiques virales (FHV) regroupent différentes maladies (Ebola, fièvre de Lassa, de Marburg, fièvre de Crimée-Congo…).
Grippe aviaire A (H5N1)
La grippe aviaire, également connue sous le nom d’influenza aviaire ou anciennement de peste aviaire, provoquée par des souches A du virus grippal, est une maladie infectieuse affectant les oiseaux sauvages et domestiques.
Hépatites virales
Les hépatites virales sont des inflammations du foie causées par un ou plusieurs virus (A, B, C, D et E).
Infections sexuellement transmissibles
Parmi les infections sexuellement transmissibles (IST), la plupart sont dues à des bactéries, des parasites ou à des virus.
Mpox
Mpox (anciennement appelé « variole du singe » ou « monkeypox ») est une maladie circulant depuis des décennies en Afrique de l’Ouest et du centre.
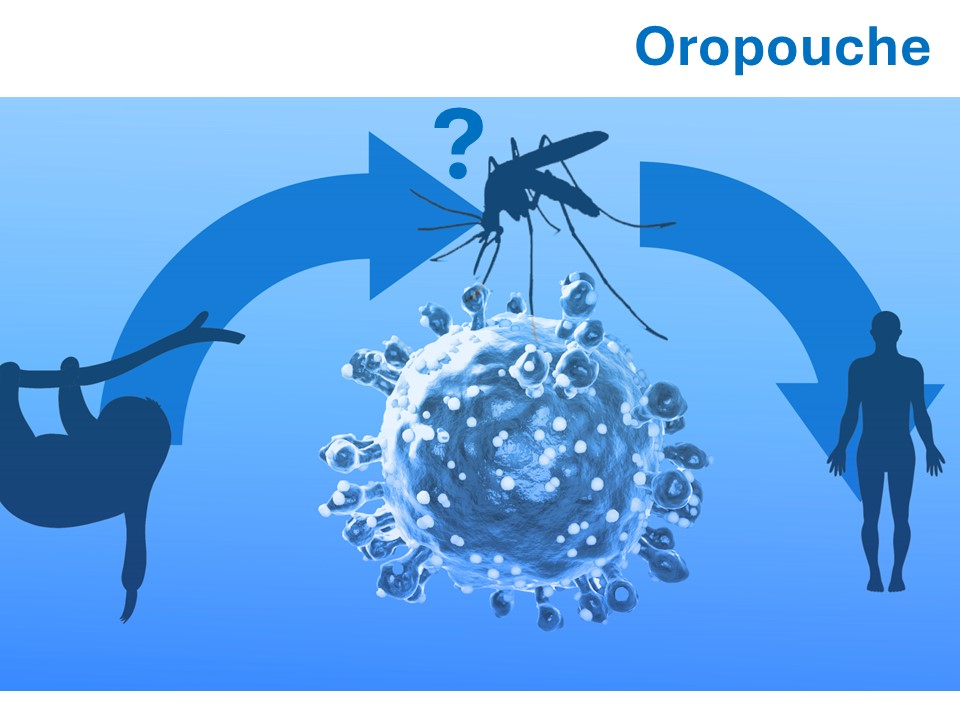
Oropouche
La maladie à virus Oropouche est une arbovirose circulant activement dans plusieurs régions d’Amérique centrale, d’Amérique du Sud et des Caraïbes.
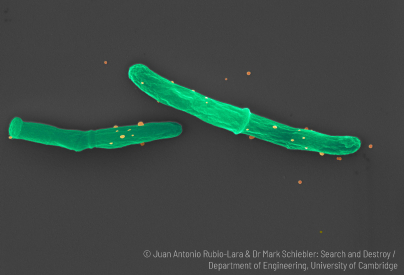
Tuberculose
La tuberculose est l’une des maladies infectieuses les plus meurtrières. Chaque jour, près de 28 000 personnes la contractent et plus de 4 100 personnes en décèdent d’après l’OMS.
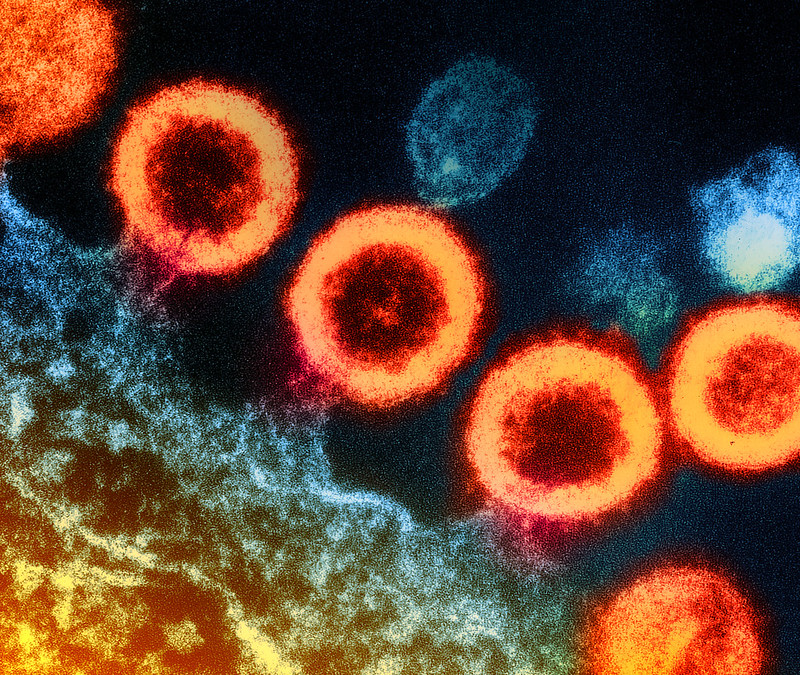
VIH et sida
Le virus de l’immunodéficience humaine (VIH), responsable du sida, touche près de 41 millions de personnes dans le monde.
